20240112乔亮PNAS
PNAS|乔亮组最新研究成果:微流控芯片与质谱技术结合揭示新抗生素治疗途径
文章题目:Molecular responses during bacterial filamentation reveal inhibition methods of drug-resistant bacteria
影响因子:12.779
发表链接:PMCID: PMC10318954 DOI: 10.1073/pnas.2301170120
样本类型:细菌细胞
涉及实验:代谢组、蛋白组
涉及软件:
- MetDNA 和 Human Metabolome Database (HMDB): 用于代谢物的鉴定
- MetaboAnalyst: 用于进行代谢统计;BioCyc: 用于进行代谢通路富集
- Spectronaut: 用于处理和分析蛋白质组学数据,帮助鉴定和定量蛋白
抗生素的广泛使用会诱发常见的 "超级细菌",即对大多数现有抗生素药物产生耐药性导致药物失效,开发新型抑菌方法至关重要。近日,复旦大学化学系乔亮团队、海军军医大学长海医院合作,在National Academy of Sciences(PNAS)上发表题为Molecular responses during bacterial filamentation reveal inhibition methods of drug-resistant bacteria的研究成果,提供了开发抑制耐药细菌的新方法。该研究利用微流控芯片技术和质谱,研究抗生素引发的细菌丝化生长与耐药性之间的关联。文章通过实时监测细菌在抗生素刺激下的代谢和蛋白组学变化,揭示了细菌耐药分子机制。易算生物协助本文进行质谱数据分析。这项研究有望为解决抗生素耐药性问题提供新的途径。
文章背景
细菌抗生素耐药性(AMR)是指随着抗生素的滥用,细菌逐渐产生对抗生素的耐药性,这对公共卫生和经济都构成了严重威胁。在抗生素的刺激下,细菌的 SOS 反应可被激活,以实现自救。丝状化这类形态变化是细菌对抗抗生素刺激的 SOS 反应之一,克服了抗生素的压力恢复生长。 通过设计适当的微芯片,可以快速分析细菌形态对抗生素的动态反应。然而,仅仅观察形态是不够的。有必要在分子水平上揭示抗生素诱导细菌 SOS 反应的各种机制。产生广谱β-内酰胺酶(ESBL)的细菌是最危险的抗生素耐药细菌之一,本项目使用在线微流控质谱系统实时表征了ESBL-E. 大肠杆菌抗生素CEF处理后,产生丝化过程中的代谢和蛋白变化。
微流控芯片的设计
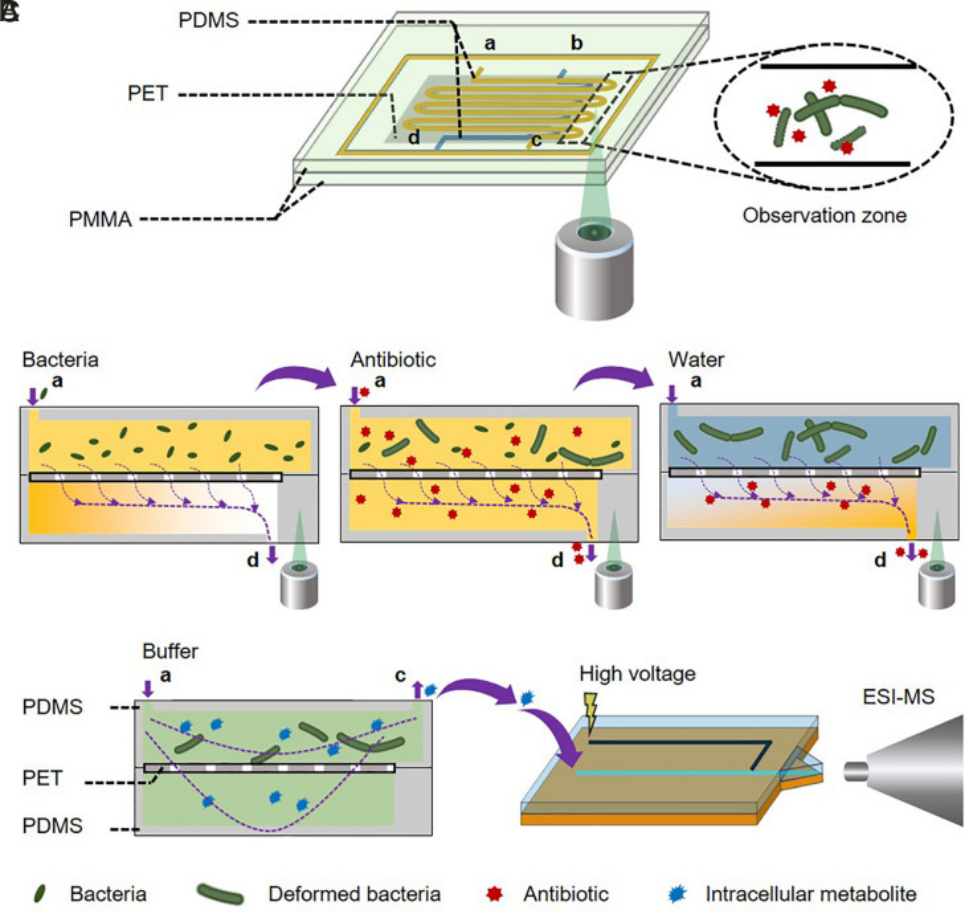
微流控质谱技术用于细菌形态变化期间细菌代谢物表征的工作流程。这个装置被设计用于在抗生素刺激下进行细菌培养。细菌被加载到微流控芯片的上层通道中。接下来,含有抗生素的培养基被注入到微流控芯片中,从而刺激细菌的生长,可以从观察区域观察到细菌纤维化的形态变化。培养的细菌在微流控芯片中原位裂解,然后通过电喷雾质谱进行实现在线代谢物分析。
细菌代谢变化
方法:
- 实验菌株: ESBL-E. coli菌株(最危险的抗生素耐药细菌之一)并置于微流控装置中。
- 用药分组:含有或不含CEF抗生素。每个组进行了六次生物重复。
- 形态观察:使用微流控芯片观察培养条件下ESBL-E. coli的细胞形态变化。有抗生素的形态会成为线状;没有抗生素处理形状会维持杆状。
- 代谢物检测:使用在线SI-MS质谱对线状、杆状组这两组细菌的代谢物实时检测
- 数据分析:识别线状、杆状组的代谢物分布、代谢差异、生物通路。代谢物鉴定使用MetDNA和HMDB
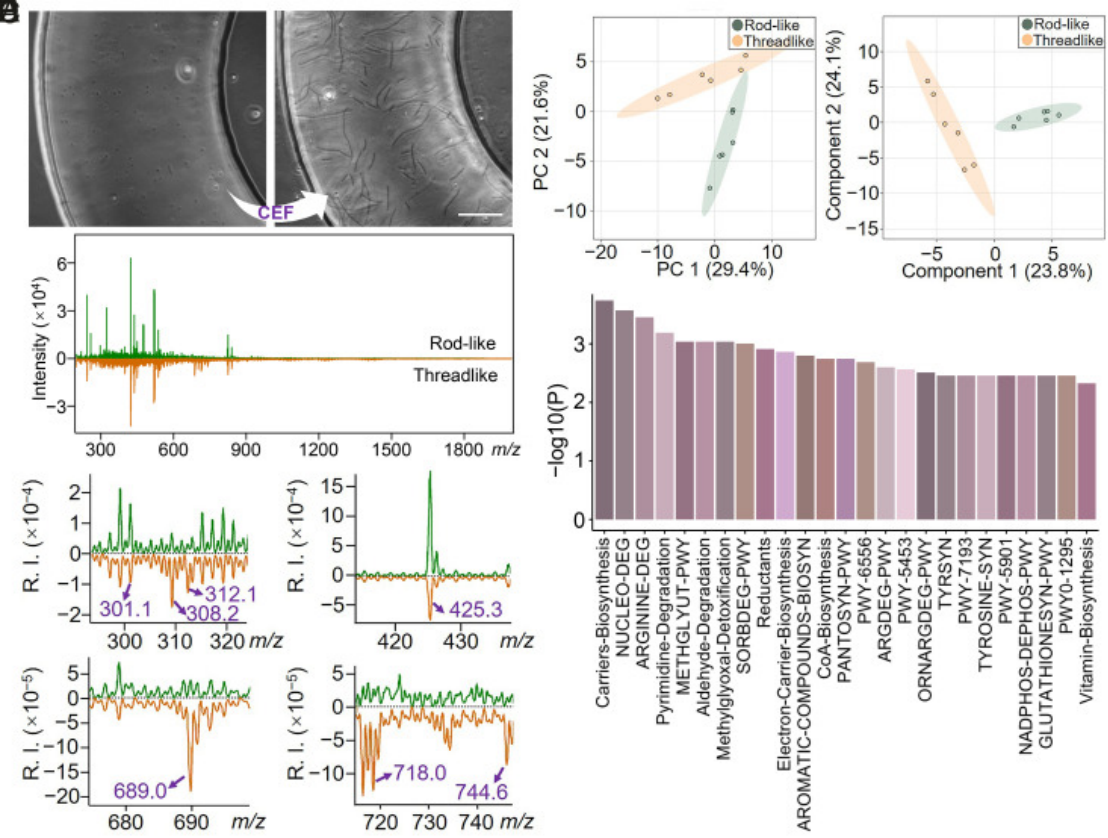
结果
- 数据分布:主成分分析(PCA)和偏最小二乘-判别分析(PLS-DA)结果显示,杆状和线状细菌细胞的质谱特征可以很好地分成两个可区分的组,表明ESBL-E. coli的代谢状态在丝化过程中发生了显著变化。
- 代谢物差异:鉴定了26种差异代谢物
- 代谢通路:BioCyc数据库显示代谢变化主要集中在核苷酸代谢、泛酮酸和辅酶A生物合成、精氨酸降解、谷胱甘肽合成等方面。
细菌蛋白变化
方法:
- 蛋白样本准备:使用与代谢组学相同的培养条件,将ESBL-E. coli细菌通过抗生素刺激与否,培养成线状和杆状细胞,分别收集。
- 蛋白提取:提取两组不同形态的细菌细胞的胞内蛋白。
- 蛋白质谱数据分析:蛋白质组学数据由 Spectronaut 处理和分析。 使用总离子色谱(TIC)进行归一化。每个组进行了三次生物重复实验。后续进行差异分析、功能分析
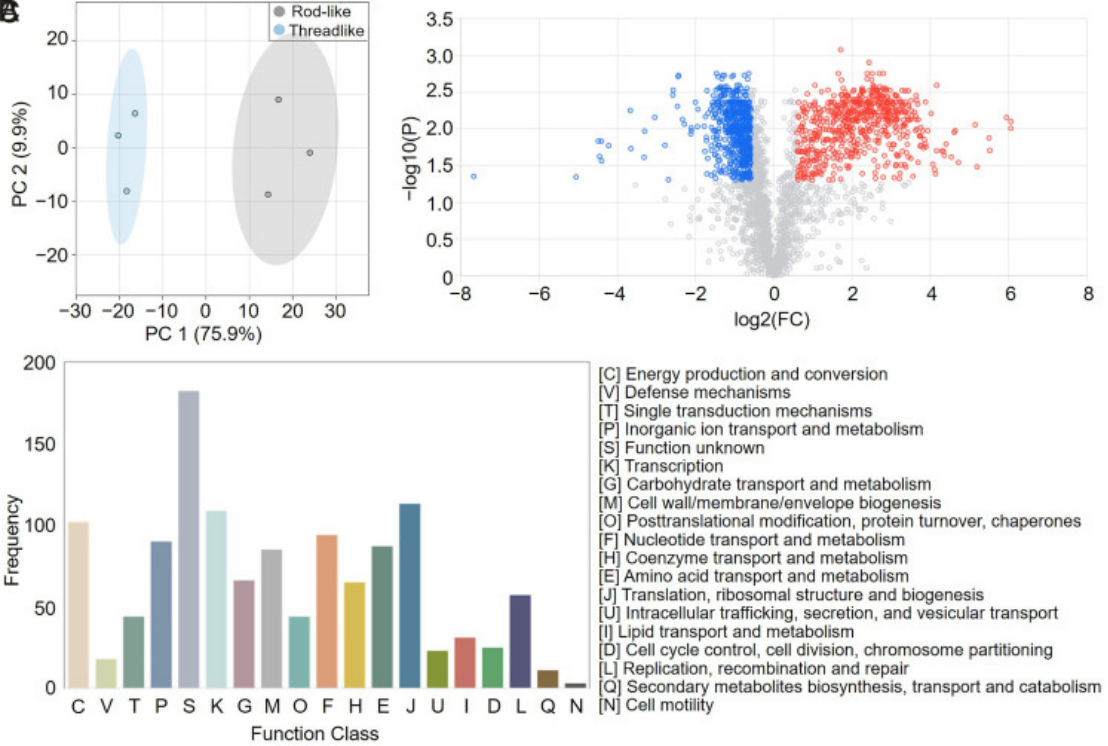
结果:
- 蛋白鉴定和定量:从线状和杆状细菌细胞中鉴定和定量了2,693种蛋白。
- 蛋白差异:根据PCA分析,线状和杆状细胞的蛋白组分为两个可区分的组,表明ESBL-E. coli的蛋白状态在纤维化过程中发生了显著变化。通过火山图,发现线状和杆状细菌细胞之间有1,212种蛋白有显著变化。
- 功能分析:利用蛋白功能类别(COG)数据库进行对显著蛋白的功能分析,发现这些蛋白主要参与能量产生和转化、氨基酸运输和代谢以及转录等功能类别。这些结果与ESBL-E. coli纤维化过程中的生物学响应相一致。
- 关键发现:在显著差异蛋白中,有85种蛋白参与了细胞壁、膜和包被的生物合成,与纤维化现象一致;核苷酸代谢和辅酶A生物合成:蛋白组学和代谢组学的结果都强调了ESBL-E. coli纤维化过程中核苷酸代谢和辅酶A生物合成的重要性。
细菌代谢、蛋白通路联合分析
方法:结合代谢物和蛋白质的富集通路结果,鉴定了辅酶A生物合成、核苷酸代谢和氨基酸代谢中的差异代谢物和蛋白。
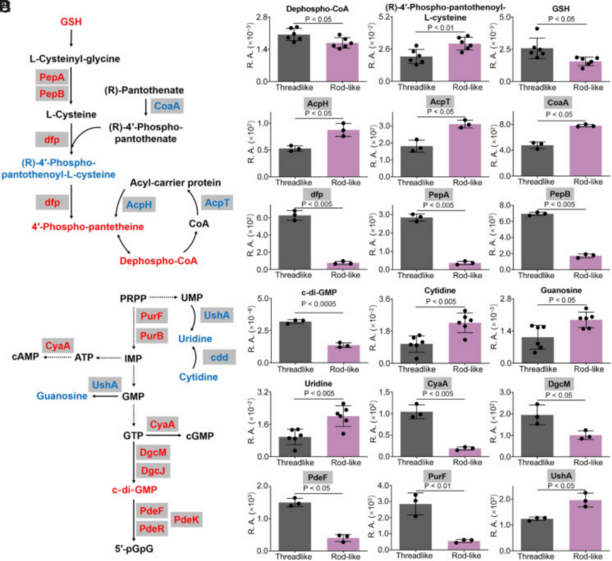 ESBL-E. coli细菌在受到抗生素刺激时,经历了显著的生化变化,特别是在辅酶A生物合成和核苷酸代谢通路中。这些通路中上下调的代谢物和蛋白质可能涉及关键的生物学过程,如细菌的抗药性和生物膜形成,为解析细菌的抗药性机制提供了线索。
ESBL-E. coli细菌在受到抗生素刺激时,经历了显著的生化变化,特别是在辅酶A生物合成和核苷酸代谢通路中。这些通路中上下调的代谢物和蛋白质可能涉及关键的生物学过程,如细菌的抗药性和生物膜形成,为解析细菌的抗药性机制提供了线索。
上面提到当这种细菌丝状生长的形态变化时,细菌的核苷酸代谢发生了变化。一个称为c-di-GMP的代谢分子在这个过程中起作用。这个分子的水平由两类酶控制,分别是DGCs和PDEs。研究中发现,在细菌丝状生长过程中,c-di-GMP的水平上升。
为了了解c-di-GMP在细菌对抗抗生素的反应中的作用,使用了一种叫做ebselen的药物来减少c-di-GMP的产生。结果显示,ebselen可以显著增加ESBL-E. coli对β-内酰胺类抗生素的敏感性。这个发现对不同类型的β-内酰胺类抗生素也适用。
另外还发现,DgcM是在细菌丝状生长期间显著上调的一个关键酶。为了证明DgcM在细菌对抗抗生素的耐受性中的作用而制备了一个没有DgcM基因的ESBL-E. coli突变株。结果显示,ebselen对这一突变株的影响较小,这表明ebselen的抑制作用主要是通过抑制DgcM和c-di-GMP的产生来提高细菌对β-内酰胺类抗生素的敏感性。
总结
- 研究中采通过微流控芯片实现了对细菌在抗生素环境下的培养和监测。这种方法不仅能够连续监测细菌的形态和生长,还能够在微流控芯片内原位裂解培养的细菌,避免了传统大规模培养实验中繁琐的离心等处理步骤。
- 该芯片还可以与质谱技术(Mass Spectrometry)相结合,实现了代谢、蛋白组的分析。特别值得关注的是,研究团队提出了一种全新的治疗策略,通过抑制特定酶的活性,提高了细菌对抗生素的敏感性。这一策略为应对耐药细菌问题提供了崭新的途径。
- 研究中使用了多个软件,如MetDNA用于代谢物鉴定,Spectronaut用于蛋白质组学数据处理。这些工具提供了与微生物生理密切相关的关键分子信息,为未来应对细菌感染和耐药性挑战提供了有力支持。
好了,以上就是今天的内容。假如你正在或者将要开展代谢、蛋白质组学方面的课题,想找到更多更有价值的信息,请你和我们联系。假如您的朋友目前有代谢、蛋白组课题的想法,想深入了解如何获得高质量的质谱代谢、蛋白组数据,也请你帮我们把这篇文章转发给他。